Imagen de portada: cultivo de bacterias Nesterenkonia amarillas, Deinococcus y Sphingomonas anaranjadas realizado por la artista Maria Penil.
—Doctora, siento que yo no soy yo. Siento que soy muchos seres a la vez... —Evidente, si usted está compuesto de muchos seres. Billones, para ser exacta.
—¿Qué dice? Yo pensé que sufría de algún trastorno de personalidad múltiple...
—No, pues. Lo que tiene usted son bacterias y otros microorganismos. En todo su cuerpo.
—Eso no puede ser. Me baño todos los días y me paso lavando las manos. —No hay nada que pueda hacer: los microorganismos están en todo su cuerpo: por fuera, por dentro, bajo sus uñas, en el pelo, en sus ojos, sus orejas, en sus intestinos... Y hasta le dicen qué debe comer.
—¿Cómo?
—Usted no es usted: usted es un mosaico de organismos. De humano tiene menos de la mitad.
Llegado a este punto, el paciente huye de la oficina, gritando desesperado.
Claro, si hubiese ido a la consulta de una doctora en psiquiatría en lugar de una doctora en biología, la historia habría sido distinta. Pero entonces nuestro pobre sujeto de pruebas nunca hubiese abierto su mente a los hechos: el mundo está dominado por minúsculas criaturas. Criaturas que no podemos ver, pero cuya presencia se siente cuando, por ejemplo, percibe ese olor agradable después de la lluvia o cuando casi se desmaya por el olor del pollo olvidado fuera del refrigerador cuando regresa a casa después de un fin de semana largo lleno de excesos.
Lo que sabemos ahora es que efectivamente el mundo está totalmente colonizado por microorganismos (lo que es una verdadera pesadilla para las personas con trastorno obsesivo compulsivo). No hay lugar en la Tierra donde no haya vida microbiana. Y es más: no podríamos existir si no fuera por ellas.
O sea, el primer mito a derribar: las bacterias no son el demonio invisible, son buena onda. No todas, por supuesto: nadie podría convivir armoniosamente con el Streptococcus pneumoniae (que puede causar neumonía, sinusitis, peritonitis...). Pero la gran mayoría de los microorganismos que habitan nuestro cuerpo son fundamentales para nosotros. Y son muchos. Muchísimos.
Las bacterias son algo así como el código de la vida. Y, como la Matrix, no son visibles a simple vista
Digámoslo así: si se hicieran elecciones para determinar quién gobierna su cuerpo, los microorganismos [Bacteria, Archaea, microeucariontes, virus] le ganarían fácilmente a las células humanas (1). Piense en la Matrix... bacterias everywhere.
Hasta el año 2016 se creía que la relación células humanas-bacterias era de 1:10 (2); ahora sabemos que es casi mitad-mitad (3). En general, un hombre de «referencia» [chiste - risas] como el paciente de nuestra historia contiene cerca de 30 billones () de células humanas y 39 billones de bacterias.
Y si las bacterias son invisibles, ¿cómo las estudiamos? ¿Ah?
A veces los microorganismos crecen de tal forma que nos damos cuenta de inmediato. Por ejemplo, cuando se nos olvida por semanas un sándwich en la mochila, los hongos se hacen evidentes. O cuando alguien no se lava los dientes por varios días (no, por favor no haga la prueba, ni siquiera como experimento), la formación de biopelículas en los dientes es notoria y amarilla. Por eso, tempranamente, la ciencia desarrolló «medios de cultivo» para «aislar» microorganismos, generalmente bacterias y hongos. De hecho, gran parte de la microbiología que conocemos está basada en el cultivo y aislamiento de microorganismos.
Pocos saben que fue una mujer, Angelina Fanny Hesse, quien creó el medio de cultivo en base a agar-agar (compuesto gelatinoso extraído desde algas marinas como el pelillo, del cual tenemos una especie en Chile: la Gracilaria chilensis). Las investigaciones de Hesse fueron la base de los trabajos de Robert Koch, quien, entre otros descubrimientos, vinculó el desarrollo de enfermedades como la tuberculosis a la presencia de bacterias.
Angelina Fanny Hesse; collage de Fruzsina Eördögh
Esta técnica es ampliamente utilizada hasta el día de hoy. Por ejemplo, una infección urinaria se detecta cultivando las bacterias que están creciendo de forma acelerada en nuestra vejiga usando medios de cultivo específicos en base a agar. Sin embargo, actualmente se sabe que menos del 1% de los microorganismos pueden ser cultivados. Es decir, la enorme mayoría de las Bacterias, Archaea, hongos y virus son desconocidos.
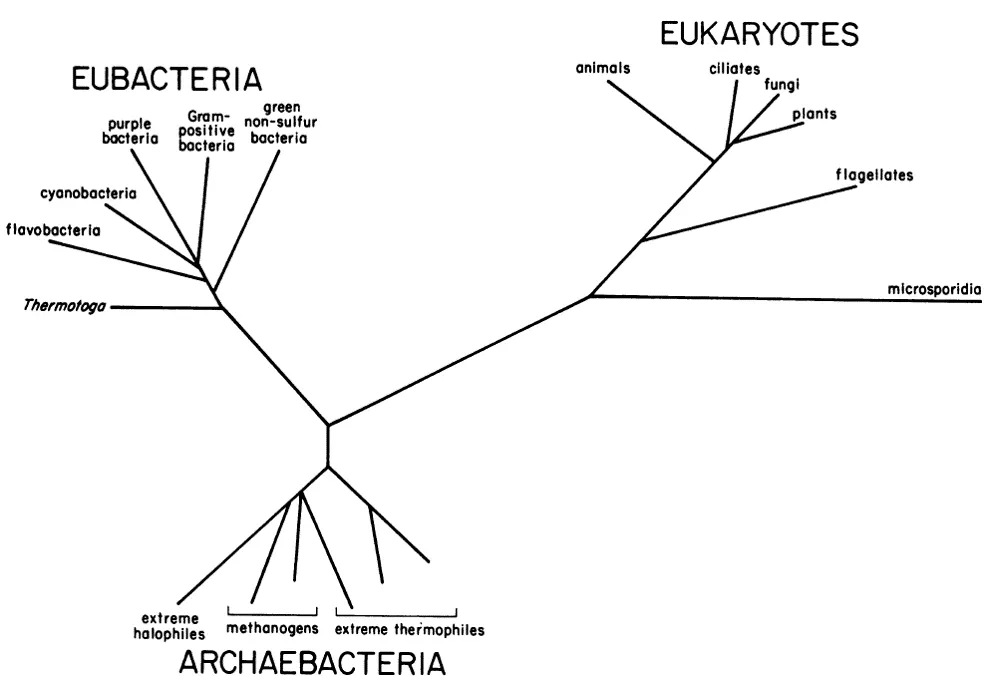
Árbol de la vida basado en secuencias parciales (es decir, no el gen completo) del gen ribosomal 16S (4)
Con el avance de la biología molecular en la década de los 70 y 80 se diseñaron marcadores genéticos para estudiar microorganismos, descubriéndose incluso un nuevo dominio de la vida: Archaea (4) [se pronuncia Arkea], que en ese entonces eran consideradas «bacterias» que vivían en condiciones «extremas» como el agua hirviendo, salmueras o ambientes muy ácidos.
En los años 90, el estudio de los microorganismos basados en su secuencia de ADN se extendió al ambiente, con el objetivo de estudiar los microorganismos que no podían ser cultivados y... Surprise, surprise, en todo ambiente que se investigaba, se encontraban microorganismos, incluso en lugares tan insospechados como las nubes (5), las minas de cobre (6) o el corazón de la vieja [cita requerida].
Fuente: imgFlip Meme Generator.
Las investigaciones que nos han permitido descubrir que los microorganismos están en todas partes han avanzado mucho en las últimas décadas junto con un sostenido avance tecnológico. Para poder estudiar los microorganismos que no se pueden cultivar, se necesita su ADN, el cual está presente en el ambiente (por ejemplo, agua de mar o saliva) para poder ser secuenciado y analizado. Cuando se comenzaron a masificar estas investigaciones, las técnicas utilizadas eran lentas y costosas. La secuenciación de genomas (el material genético de un organismo) o metagenomas (distintos genomas en una determinada muestra) involucraba grandes esfuerzos monetarios y tiempo. Aun así, se alcanzaron hitos importantes, como la secuenciación del genoma humano (7 y 8), cuyo borrador tardó diez años en completarse; o la secuenciación del Mar de los Sargazos mediante técnicas de metagenómica (9).
Durante la segunda mitad de la década del 2000 se desarrollaron técnicas de secuenciación «de nueva generación» o NGS por sus siglas en inglés (Next Generation Sequencing), que permiten realizar de forma masiva y paralela miles de reacciones de secuenciación a la vez, gracias al principio de «secuenciación por síntesis». Las hay de varios colores y sabores, e incluso algunas ya están casi obsoletas (como la pirosecuenciación que comercialmente estuvo disponible sólo por 6 años). Actualmente se desarrollan técnicas de secuenciación basadas en nanotecnología, lo cual ha reducido los costos en forma notoria y ya es posible tener un secuenciador de ADN de bolsillo como el MinION de la empresa Oxford Nanopore (10).
Mucho entusiasmo provoca el secuenciador de ADN de bolsillo MinION.
Este es un ejemplo claro de cómo los descubrimientos y desarrollos tecnológicos de un área benefician el avance de otras. Algo parecido a lo que significó pasar del ábaco a la calculadora, y de ahí al computador. Y nadie puede negar lo fundamental que se ha vuelto el computador en la investigación científica.
Volvamos a la matrix. Lo que estas «técnicas independientes de cultivo» y de «secuenciación masiva» permiten no solo es acceder a estudiar «la mayoría no cultivable», sino que también comprender que en cada espacio, respiro o tecla del computador hay un universo microbiano por descubrir.
Actualmente, se usa el término «microbioma» para definir al hábitat donde viven las comunidades microbianas. Es decir, si queremos saber qué bacterias viven asociadas al querido teléfono celular que probablemente esté usando en este momento, será el microbioma del celular (12). Es así como surgen por el 2010 proyectos de secuenciación a gran escala como el «Human Microbiome Project» (proyecto microbioma humano) que involucró el estudio de microorganismos que habitan el cuerpo humano (1) y otros como el Earth Microbiome Project (Proyecto Microbioma de la Tierra) (11) o el American Gut - Human Food Project.
¿Bacterias en mi cuerpo? ¡Pero si me bañé ayer!
Las bacterias y otros microorganismos colonizan la mayoría de los rincones de nuestro cuerpo. Cuando caminamos dejamos una estela microbiana, que es nuestra huella inconfundible. Cada individuo tiene una marca microbiana única (13).
Fuente: http://learn.genetics.utah.edu/content/microbiome/changing/
El intestino es el ambiente predilecto para billones de bacterias de distintos tipos que viven en comunidad, degradando los alimentos que ingerimos. Es decir, por cada cosa que usted come hay una bacteria (o un grupo de bacterias) específica esperando darse un festín, desarmando y transformando los alimentos. Lo que este tipo de bacteria produce puede ser usado a su vez por otro tipo de microorganismo, generando una verdadera comilona intestinal. Por eso no tiene sentido tomar jugo de limón en ayunas para «cambiar el pH del cuerpo y combatir el cáncer». Se les olvida (o no saben) que existe el microbioma que media en gran parte los procesos fisiológicos y metabólicos del organismo.
Cuando duele la guatita, lo más probable es que se deba a que la comunidad bacteriana está perturbada o en desequilibrio («disbiosis»). Cuando la microbiota intestinal se regenera, todo vuelve a la normalidad y nos sentimos de maravilla.
Está en discusión la presencia de un microbioma único para ambientes con bajo número de microorganismos como la placenta, que se creía «estéril» (14 y 15). Cuando nacemos, venimos a este mundo con una concentración baja de bacterias que han sido adquiridas directamente de la madre. Las bacterias que se alojan en el intestino son específicas para degradar los componentes de la leche materna humana. De hecho, se han reconocido más de 200 oligosacáridos distintos en la leche materna (16) que actúan como prebióticos para el establecimiento de bacterias beneficiosas, protegiendo a los bebés de infecciones por bacterias patógenas (17). Por eso no da lo mismo que una guagua tenga lactancia materna o consuma leche de fórmula para el desarrollo de su microbiota intestinal. Tampoco da lo mismo la forma en que nacemos: se ha demostrado que hay diferencias en la composición microbiana de bebés que nacen por parto natural o cesárea (18). Incluso se han vinculado estas diferencias a problemas futuros de salud como la obesidad o colon irritable (19).
La mayoría de los estudios de microbioma humano se han realizado en el intestino y en la piel. Llama la atención la presencia de bacterias «insospechadas» en lugares aun más insólitos, como cianobacterias en el dedo gordo del pie (realizando fotosíntesis a través del calcetín) y una selva de bacterias en el ombligo (o «pupo», como le decimos en el Norte de Chile).
Todo este conocimiento está cambiando la forma de pensar la biología humana. Usted ya no es usted y sus circunstancias, sino usted-sus bacterias [y los otros invisibles] y su entorno que interactúan a distintos niveles.
Así que si hoy saludó a su colega de la mano, comprenda que tiene adheridas miles de sus bacterias y que en este momento sus bacterias intestinales están degradando molécula por molécula la sopaipilla con mostaza que se comió. Ni hablar si lo saludó de beso. Con mirada microbiana, el mundo ya no es el mismo.
Esta historia continuará...
Referencias
1.
Turnbaugh PJ, Ley RE, Hamady M, Fraser-Liggett CM, Knight R, Gordon JI (2007) The Human Microbiome Project. Nature 499: 804-810
2.
Luckey T (1972) Introduction to intestinal microecology. Am J Clin Nutr 25:12 1292-1294
3.
Sender R, Fuchs S, Milo R (2016) Revised estimates for the number of human and bacteria cells in the body. PLoS Biol 14(8): e1002533
4.
Woese C (1987) Bacterial evolution. Microbiol Rev 51(2):221-271
5.
Möhler O, DeMott PJ, Vali G, Levin Z (2007) Microbiology and atmospheric processes: The role of biological particles in cloud physics. Biogeosciences 4(6):1059–1071.
6.
Goebel BM, Stackebrandt E (1994) Cultural and phylogenetic analysis of mixed microbial populations found in natural and commercial bioleaching environments. Appl Environ Microbiol 60(5):1614-1621
7.
Lander S, et al. (2001) Initial sequencing and analysis of the human genome. Nature 409(6822):860-921.
8.
Venter JC, et al. (2001) The Sequence of the Human Genome. Science 291(5507): 1304-1351.
9.
Venter JC, et al. (2004) Environmental genome shotgun sequencing of the Sargasso Sea. Science 304(5667):66-74.
10.
Eisenstein M (2012) Oxford Nanopore announcement sets sequencing sector abuzz. Nature Biotechnology 30: 295–296.
11.
Caporaso JG, Lauber CL, Walters WA, Berg-Lyons D, Lozupone CA, Turnbaugh, PJ, … Knight R (2010). Global patterns of 16S rRNA diversity at a depth of millions of sequences per sample. Proc. Natl Acad. Sci. USA 108(Supplement_1), 4516–4522.
12.
Meadow JF, Altrichter AE, Green JL (2014) Mobile phones carry the personal microbiome of their owners. PeerJ 2: e447.
13.
Meadow JF, Altrichter AE, Bateman AC, Stenson J, Brown GZ, Green JL, Bohannan JM (2015) Humans differ in their personal microbial cloud. PeerJ. 3: e1258.
14.
Lauder AP, Roche AM, Sherrill-Mix S, Bailey A, Laughlin AL, Bittinger K, Leite R, Elovitz MA, Parry S, Bushman FD (2016) Comparison of placenta samples with contamination controls does not provide evidence for a distinct placenta microbiota. Microbiome 4:29
15.
Perez-Muñoz ME, Arrieta MC, Ramer-Tait AE, Walter J (2017) A critical assessment of the "sterile womb" and "in utero colonization" hypotheses: implications for research on the pioneer infant microbiome. Microbiome 5(1):48
16.
German JB, Freeman SL, Lebrilla CB, Mills DA (2008) Human milk oligosaccharides: evolution, structures and bioselectivity as substrates for intestinal bacteria. Nestle Nutr Workshop Ser Pediatr Program 62:205–218 [discussion 18–22].
17.
Ward RE, Ninonuevo M, Mills DA, Lebrilla CB, German JB (2006) In vitro fermentation of breast milk oligosaccharides by Bifidobacterium infantis and Lactobacillus gasseri. Appl Environ Microbiol 72(6):4497–4499.
18.
Dominguez-Bello, M. G. et al. (2010) Delivery mode shapes the acquisition and structure of the initial microbiota across multiple body habitats in newborns. Proc. Natl Acad. Sci. USA 107, 1971–11975.
19.
Greenblum S, Turnbaugh PJ, Borenstein E (2012) Metagenomic systems biology of the human gut microbiome reveals topological shifts associated with obesity and inflammatory bowel disease. Proc. Natl Acad. Sci. USA 109, 594–599.